医学报告软件 virSEAK导入NGS分子生物
添加到我的收藏夹
添加到产品对比表
fo_shop_gate_exact_title
产品规格型号
- 功能
- 报告, 导入, NGS
- 应用
- 分子生物
- 类型
- 自动化
产品介绍
virSEAK(RUO - 仅供研究使用)提供快速和方便的SARS-CoV-2序列与现有序列的比较。在对你的试剂盒进行个性化设置后,只需加载fastq或fasta数据,就可以得到一个与变异体对齐的序列。
此外,你的序列将被分配到一个穿山甲系(如B.1.1.7)和一个GISAID支系(如L)。
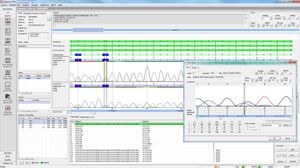
virSEAK也会自动检查你的序列是否含有穗状蛋白变体N501Y和或E484K。
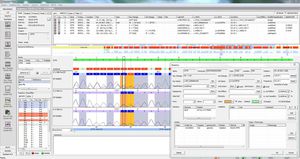
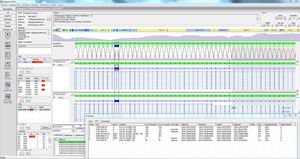
覆盖率和质量值显示,包括:要求的、绝对的、平均的和中位的覆盖率,"野生型 "和 "N "碱基的百分比。质量指标显示质量是否满足定义的质量阈值。
此外,该工具还为高通量NGS测序进行了优化,具有自动导入和导出功能以及可定制的序列转移。轻松地创建多fasta文件,以改进向中央报告办公室的报告,用于监测流行病学情况和突变的传播(例如对德国的Robert Koch研究所)。
virSEAK - 可安装版本:
轻松导入原始fastq或预处理的fasta测序文件
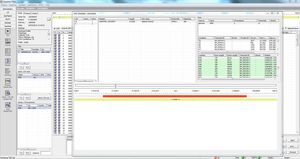
高通量NGS测序,自动批量导入和导出
如果包含N501Y和/或E484K的突变,自动发出警报
获得对穿山甲血统和GISAID支系的分配
检查其他变异的频率
比较发现的亚型、数量和位置,...
输出序列和变异体(带元信息,以fasta和/或csv格式)。
储存结果
完全自动化的高通量测序,可定制的序列转移
---
PDF产品目录
该产品还没有PDF产品手册
查看JSI medical systems的所有产品目录